
第一作者:Fulin Shao
通讯作者:李伟英 教授
通讯单位:同济大学环境科学与工程学院
论文DOI:10.1016/j.watres.2026.125499
逻辑链条
广泛背景(高级氧化技术AOPs广泛应用) → 核心问题(AOPs会产生大量未知毒性的转化产物TPs)→ 现有方法及其局限(传统QSAR模型依赖2D描述符,忽略了决定毒性的关键3D分子构象和电子特征,预测不准)→ 指出现有理解的不足(2D模型无法区分立体异构体等毒性差异巨大的分子,导致风险评估存在巨大盲区)→ 提出本文核心概念和策略(开发3D感知、多模态深度学习框架ToxD4C和Tox-Agents平台)→ 阐述核心机制(融合3D分子几何、图注意力网络和SE(3)-等变Transformer架构,直接从分子三维结构推断毒性)→ 预告研究成果(新框架性能超越传统模型,并结合体外实验验证了其在真实水体AOPs场景中识别高风险TPs的有效性)。
详细点评
话不多说,今天这篇文献的主角,我相信做环境化学和毒理学的老师同学都再熟悉不过了——QSAR毒性预测。在各大期刊上,通过各种分子描述符和机器学习算法来预测化学品毒性的文章屡见不鲜,比如用分子指纹、拓扑指数,再结合随机森林、支持向量机等。按理说,这个领域似乎已经被研究得很透彻了。
那么,作者是如何在这样一个“老”问题上“鸡蛋里挑骨头”,还能挖掘出新的科学内涵,并发表在环境顶刊上的呢?这就引出了一个科研非常重要的点:抓住现有方法的根本局限!
传统QSAR就像是“看图识人”,只看二维照片(2D分子结构),却忽略了人的立体轮廓、姿态和神情(3D构象、电子云分布)。这种“降维打击”在很多情况下是失效的,比如对于手性分子,它们的2D结构完全相同,但毒性可能天差地别。作者敏锐地抓住了这个“阿喀琉斯之踵”,直接宣告:2D描述符的时代该过去了!
这篇关于ToxD4C框架的文章,恰恰就是这种“升维思考”的一个绝佳体现。它没有停留在优化现有2D描述符或算法的“微调”上,而是直接引入了前沿的3D深度学习架构,从根本上改变了模型看待分子的方式。它不再是“数”基团,而是“看”构象,直接从决定分子间相互作用的物理本质——三维空间结构和电子特征出发来学习毒性。这就像从看照片升级到了用CT扫描,信息的丰富度和准确性实现了质的飞跃。
理论计算分析:
我们再看这篇文章的理论计算部分,作者团队的操作堪称“虚拟实验与现实世界的无缝衔接”,远非简单的“算个构象”!他们将理论计算从一个验证工具,升格为了一个动态的、贯穿始终的“毒性变化追踪器”。
首先,计算起点精准且务实。作者没有孤立地计算单个分子,而是紧密结合实际的水处理场景——高级氧化过程(AOPs)。他们关注的是反应过程中动态生成的、结构复杂的转化产物(TPs),这些TPs往往是实验难以捕捉和表征的“幽灵分子”。计算直接瞄准了这个核心痛点。
其次,计算目的明确,直击要害。整个计算逻辑围绕着一个核心问题:分子的三维结构和电子性质在化学转化过程中如何动态影响其毒性?
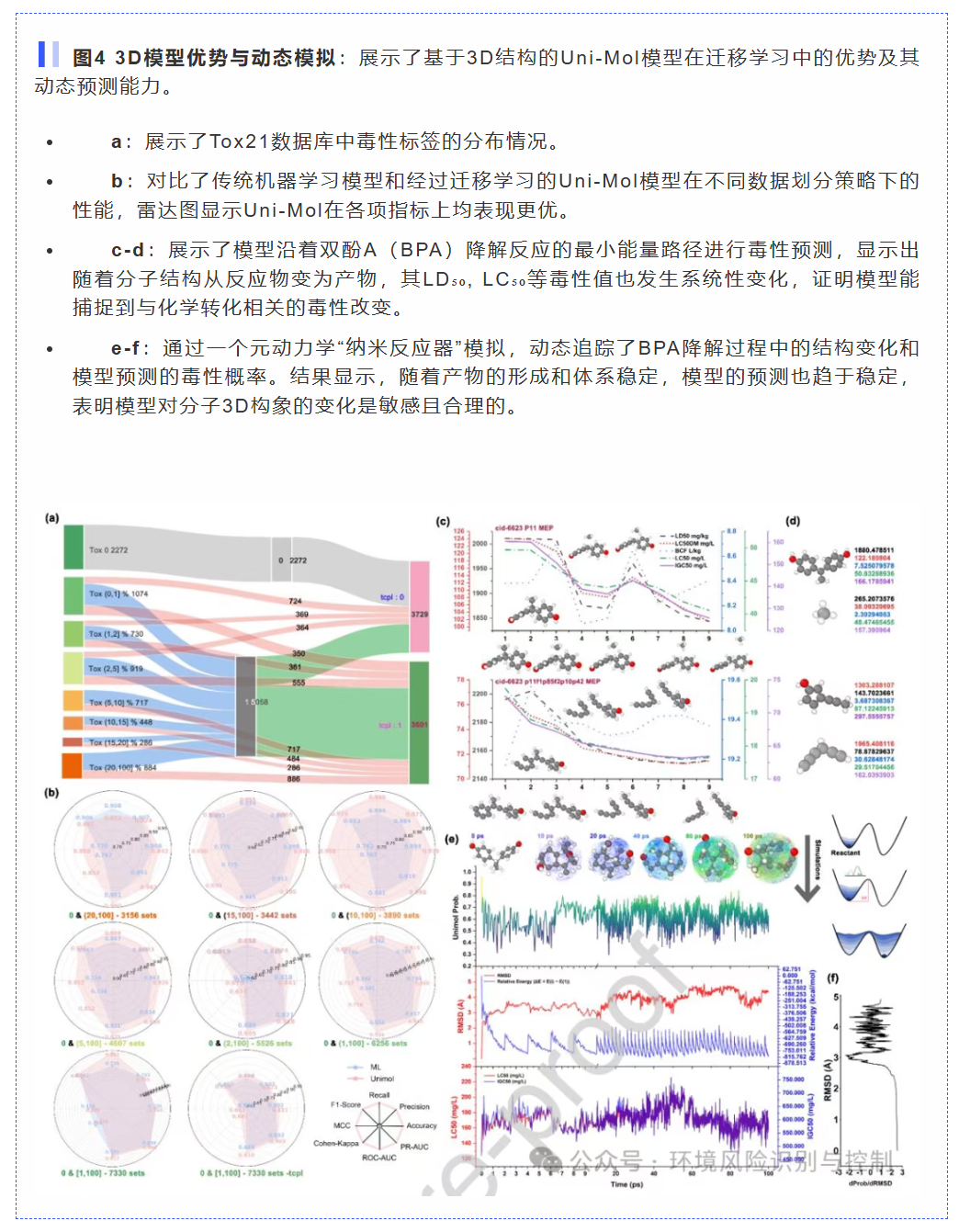
从静态到动态的毒性评估(图4c-d): 这是点睛之笔。作者不再满足于只预测反应物和最终产物的毒性,而是沿着双酚A(BPA)降解的“最小能量路径(MEP)”,实时追踪LD₅₀, LC₅₀, BCF等多个毒性终点的变化。这就像给化学反应装上了一个“毒性仪表盘”,清晰地展示了毒性是如何随着分子构象的扭转和化学键的断裂/形成而“进化”的。这种动态视角对于理解“中间产物可能比母体更毒”这一关键环境问题至关重要。
模拟真实反应环境的“纳米反应器”(图4e): 这是最大胆、最创新的部分。作者利用“元动力学(Metadynamics)”技术,构建了一个虚拟的“纳米反应器”。在这个反应器里,BPA分子在模拟的高级氧化条件下自由翻滚、碰撞、分解。模型则像一个“鹰眼”实时监控,同步输出分子的能量、结构变化(RMSD)以及毒性概率(Uni-Mol probability)和LC₅₀/IGC₅₀值。我们能直观看到,随着反应进行、产物逐渐稳定,毒性预测值也趋于平稳,这完美模拟了从高能反应中间体到稳定产物的毒性演变过程,极具说服力。
量化结构变化与毒性的敏感度(图4f): 作者更进一步,计算了毒性概率对结构变化的导数(dProb/dRMSD)。这相当于在问:“分子的结构稍微‘扭’一下,它的毒性会变化多快?”。这个分析揭示了模型的敏感性和鲁棒性,也从侧面说明了为何基于3D构象的模型比2D模型更强大——因为它能捕捉到这些对毒性至关重要的细微几何变化。
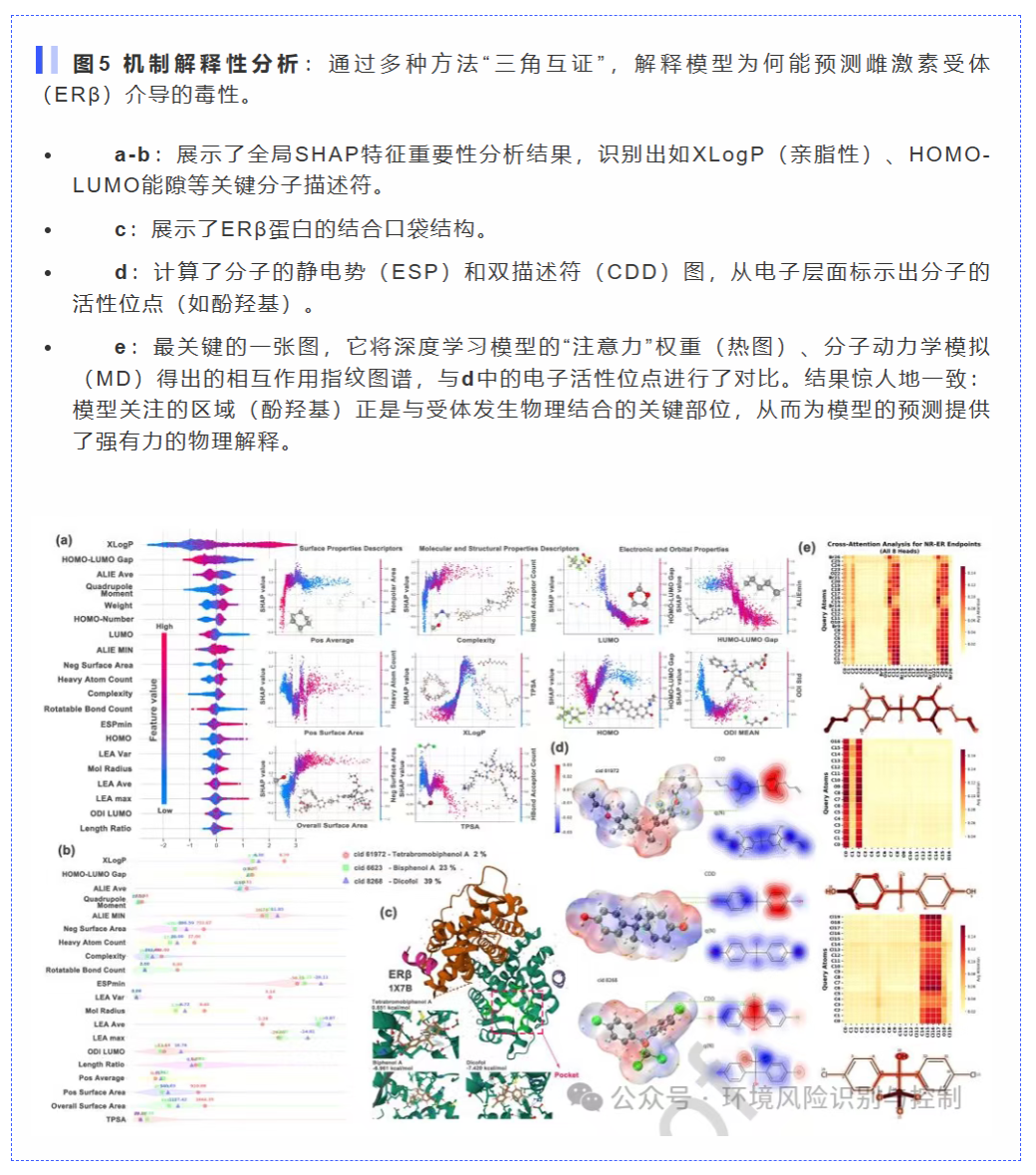
从“黑箱”到“透明”的机理解释(图5): 最精彩的部分在于,作者没有止步于预测“毒不毒”,而是要搞清楚“为什么毒”。他们通过“机理三角验证法”,将深度学习的注意力权重(模型认为哪里重要)、DFT计算的电子反应性图谱(ESP/CDD,化学上哪里活泼)以及分子对接的相互作用指纹(物理上如何结合)完美地统一起来。结果惊人地一致:模型关注的酚羟基和卤代环区域,恰好是电子云最富集/亏缺的地方,也正是与雌激素受体(ERβ)结合最紧密的“热点区域”。这套组合拳,把一个看似“黑箱”的AI预测,变成了一个有物理化学基础、可解释的科学结论。
总而言之,这篇论文的理论计算部分不是实验的附属品,而是一场深刻的、动态的虚拟毒理学探究。它从“化学反应路径”这一动态过程出发,通过“3D构象与电子结构”这一桥梁,最终完美解释了“转化产物毒性的动态演变与分子机理”这一宏观环境安全问题。整个论证过程将AI预测与物理化学原理深度融合,充分展现了计算科学在主动式、预测性环境风险评估中的强大力量。
摘要是文章的“精华浓缩版”,咱们按照“背景-问题-方案-亮点-意义”的框架来解析:
研究背景: 在水处理(特别是高级氧化过程AOPs)和水环境中,新兴污染物会转化成各种各样的副产物(TPs)。快速准确地评估这些化学物质的毒性是一个重大的环境挑战。
存在的挑战/问题: 传统毒性预测方法(QSAR)依赖于简化的二维分子描述符,这限制了它们的预测能力,尤其无法捕捉决定生物活性的关键三维空间结构特征(如立体化学)。
核心方案:
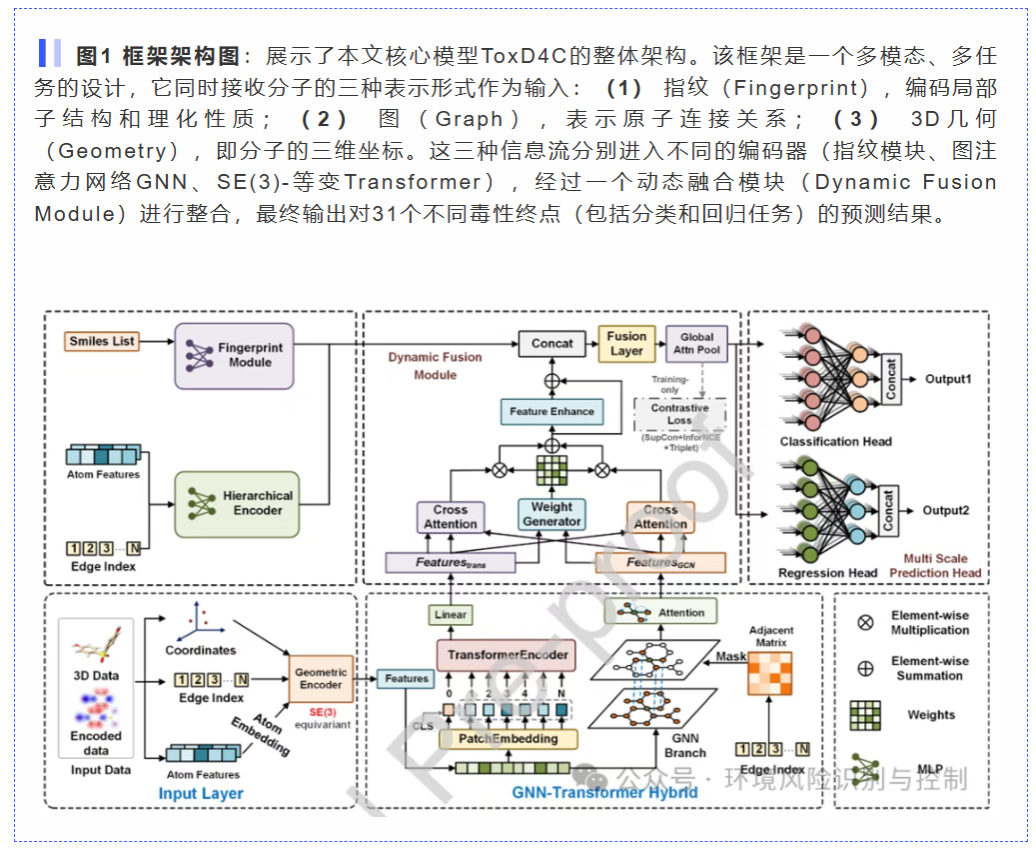
开发了一个名为ToxD4C的新型多模态深度学习框架。它不只看2D结构,而是独特地整合了三维分子几何构象、图注意力网络和SE(3)-等变Transformer架构。
并行地,利用迁移学习,在一个大型预训练模型Uni-Mol的基础上,使用DFT计算优化的分子结构进行微调,以增强预测的可靠性和泛化能力。
方法亮点:
3D感知: 模型能直接从分子的三维坐标学习,有效捕捉立体化学和电子特征,性能优于传统模型。
机理解释: 结合SHAP分析和分子对接,不仅给出毒性预测,还能揭示其背后的物理化学驱动因素和与生物靶点(如受体)的相互作用机制。
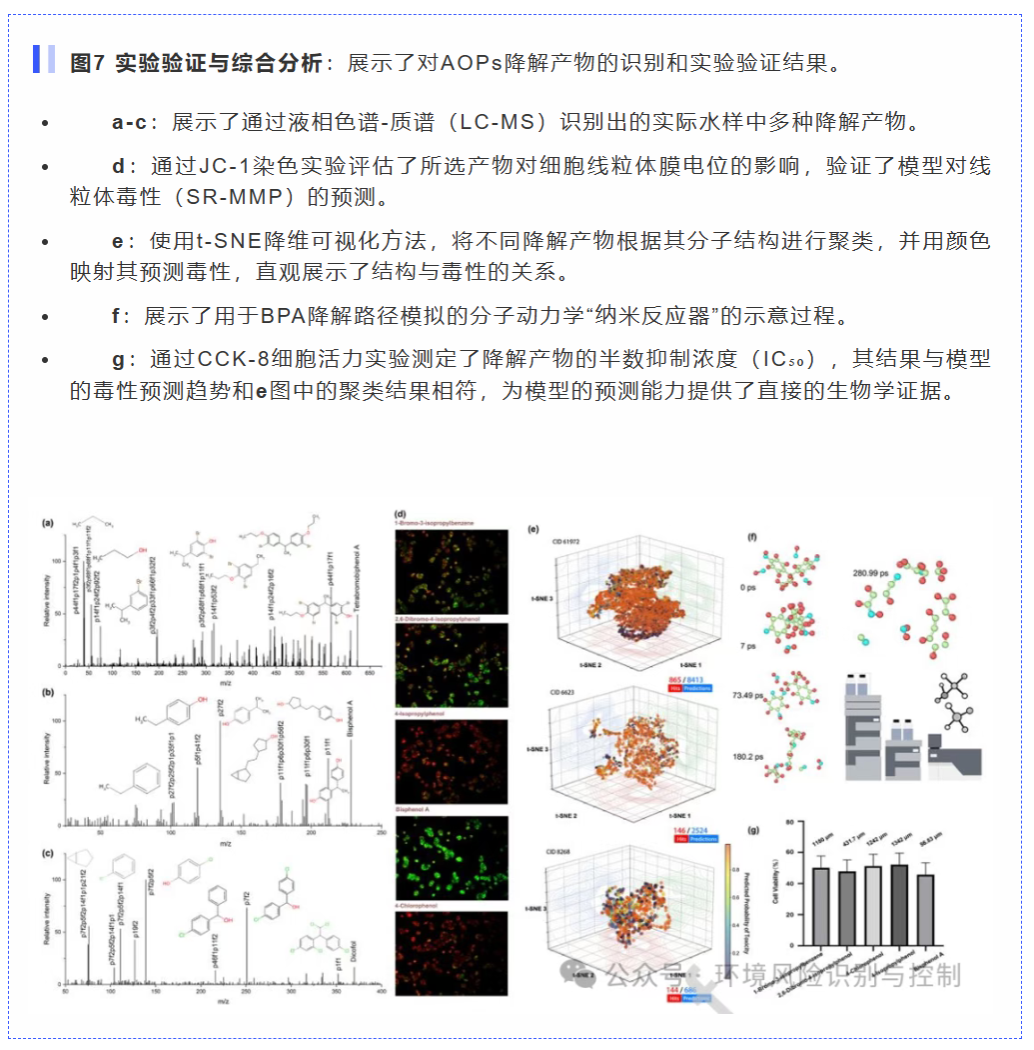
实践验证: 将该方法应用于真实的UV/H₂O₂高级氧化场景,成功识别出高风险转化产物,并通过体外细胞实验(JC-1, CCK-8等)验证了模型的预测结果。
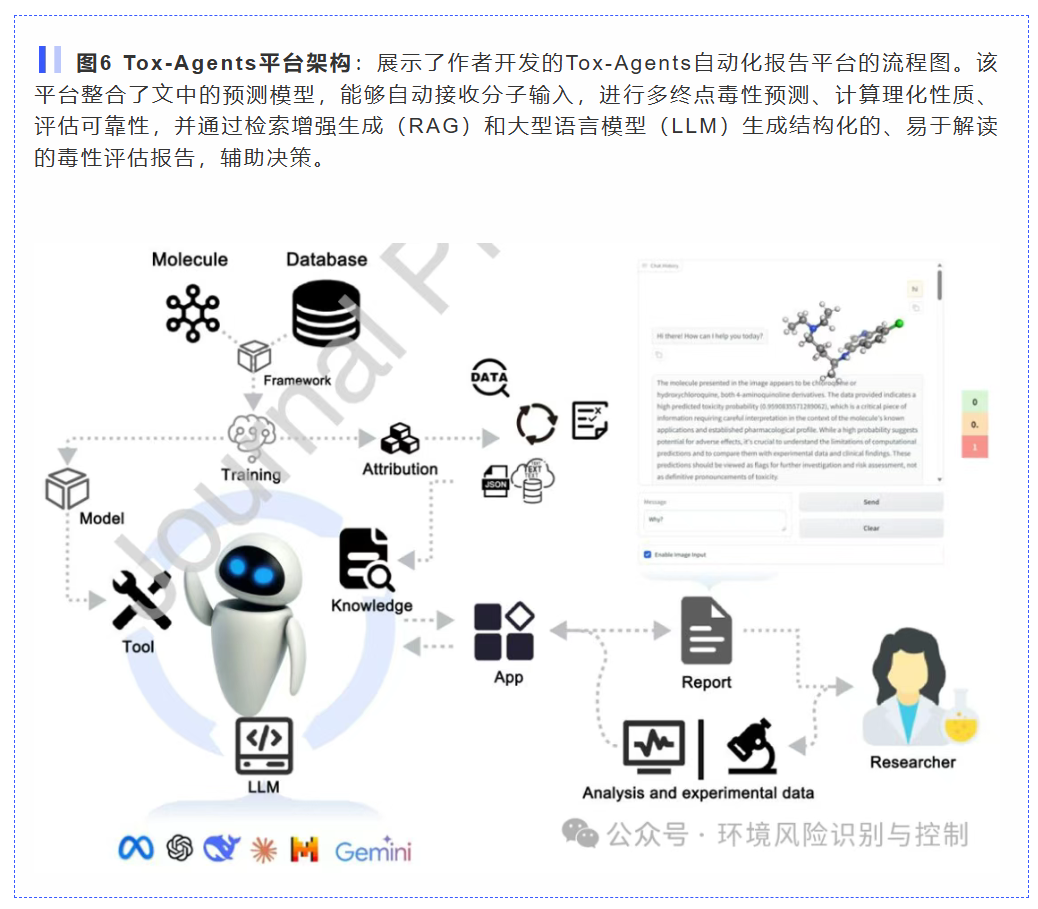
价值与意义: 开发了一个开源平台Tox-Agents,集成了这些工具。它能够为水处理和环境风险评估提供快速、可解释的决策支持,帮助我们避免在处理污染物的过程中意外制造出“更毒”的副产物。
研究亮点与数据支撑
本研究的创新解决之处:这篇文章的核心突破在于“用3D深度学习打破了传统毒性预测的‘平面化’束缚”。它不再将分子视为一张平面的连接图,而是看作一个在三维空间中具有特定形状、电荷分布的实体,从而更精准地模拟分子与生物靶点的“钥匙-锁”相互作用,实现了从“猜毒性”到“懂毒性”的跨越。
研究亮点与数据支撑(证据链):
证据一(模型性能优越性):
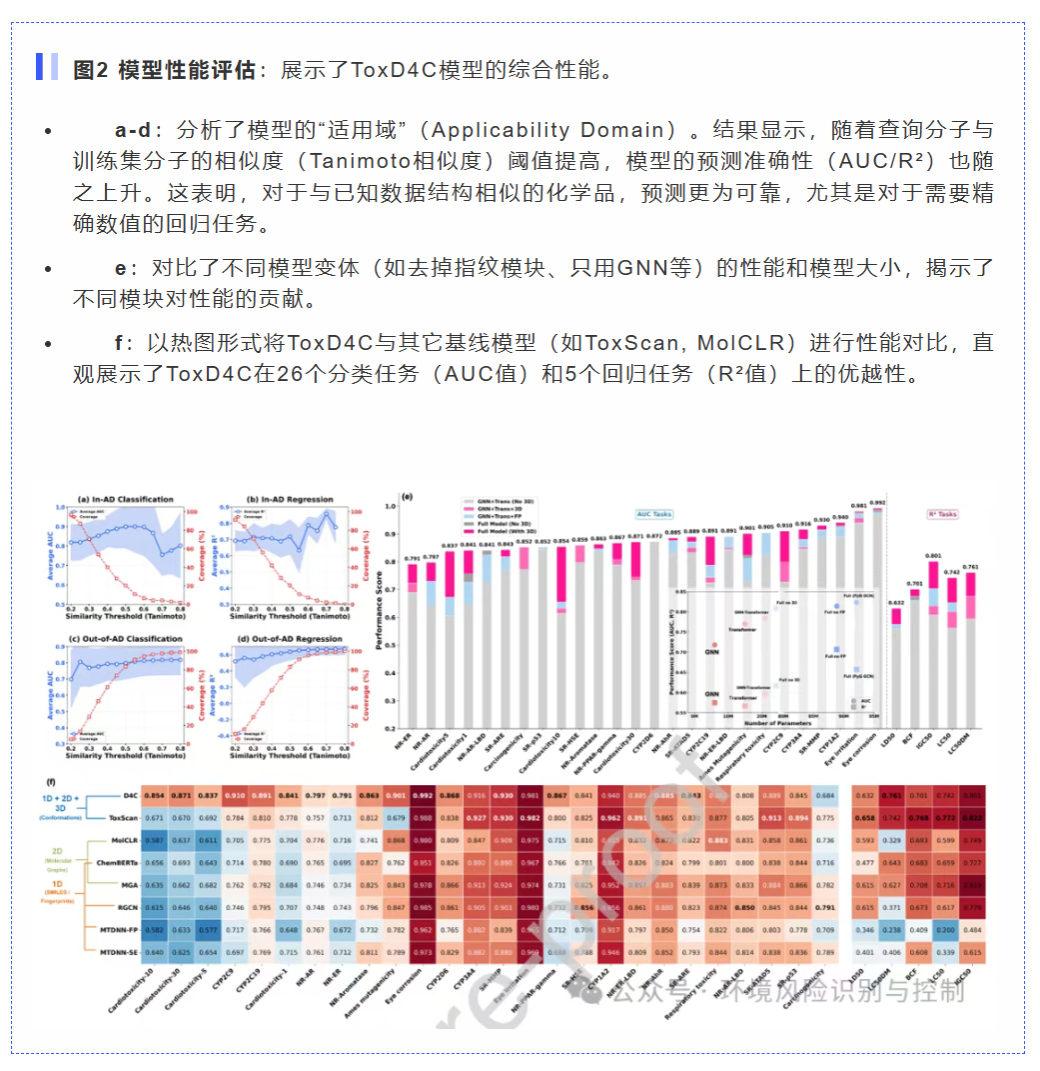
基准测试(图2f): 在包含31个毒性终点的全面基准测试中,ToxD4C的平均AUC达到0.845,优于ToxScan(0.827)等现有方法。在关键的环境终点上表现尤其出色,如生物浓缩系数(BCF)的R²值为0.701。
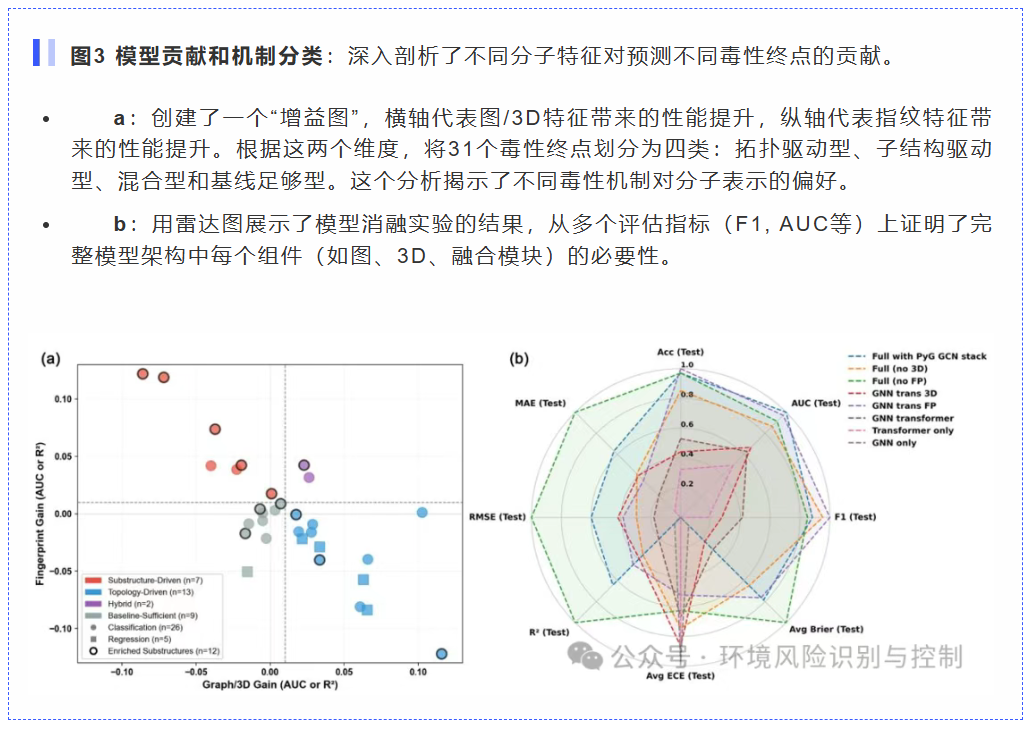
架构的必要性(图3): 通过“消融实验”证明,对于依赖分子整体形状和空间构象的毒性终点(如CYP3A4和NR-PPAR-γ),3D特征的引入带来了高达0.1157的性能增益,证实了3D信息的不可或缺性。
证据二(3D结构的重要性):
动态毒性追踪(图4c-f): 在模拟BPA降解的反应路径上,模型能够根据分子三维构象的连续变化,预测出毒性指标(如LC₅₀)的平滑演变。这在2D模型中是无法实现的,有力地证明了模型学到的是真实的“构效关系”,而非简单的碎片记忆。
迁移学习增强(图4b): 基于DFT优化的3D结构微调的Uni-Mol模型,在各项指标(ROC-AUC, PR-AUC等)上全面超越了传统的机器学习基线模型,再次印证了高质量3D信息对提升预测精度的关键作用。
证据三(从预测到机理的可解释性):
多维证据的统一(图5): 论文展示了AI模型的注意力热图、DFT计算的电子云分布图和分子动力学模拟的受体结合位点高度重合。这意味着AI模型“关注”的分子区域,正是化学上最活泼、物理上与生物靶点结合最紧密的部分。这为AI的“黑箱”预测提供了坚实的物理解释。
关键描述符的识别(表1): 通过SHAP分析,量化了如XLogP(疏水性)、HOMO-LUMO能隙(反应活性)等物理化学参数对毒性的贡献阈值,将抽象的预测与可测量的分子属性联系起来。
证据四(从理论到现实的闭环验证):
证据视觉链
详细总结文献中所有图的主要内容: 一共7个图
文献引用:1 F. Shao, W. Li, Z. Liang, Y. Zhou, D. Zhang, Y. Chang, Screening toxic transformation products of emerging pollutants in advanced oxidation processes with 3D deep learning and in vitro assays, Water Research (2026), doi: https://doi.org/10.1016/j.watres.2026.125499.